ForeSNP Genotipatzeko Kita
Zehaztapenak
Competitive Allele Specific PCR (Competitive Allele Specific PCR) teknologia aleloen idazketa metodo berri bat da.Metodo honek ez du SNP eta inDel bakoitzerako zunda espezifikoak sintetizatu behar, baizik eta bi zunda unibertsal bakarra behar ditu DNA genomikoaren laginen tipifikazio zehatza lortzeko.Azken fluoreszentzia-seinalearen intentsitatea eta ratioa aztertuz, genotipoa automatikoki zehazten da eta clustering-efektua bisualki bistaratzen da.Metodo honek detekzio denbora laburra, erreaktiboen kostu baxua, detekzio-zehaztasun handia du eta markatzaile molekularrekin lagundutako hazkuntzarako, QTL posizionamendurako, markatzaile genetikoak identifikatzeko eta biologia molekularra lagin bolumen handiko beste esperimentuetarako erabil daiteke.
Zehaztapenak
5ml, 50ml, 50ml × 10, 500ml × 20
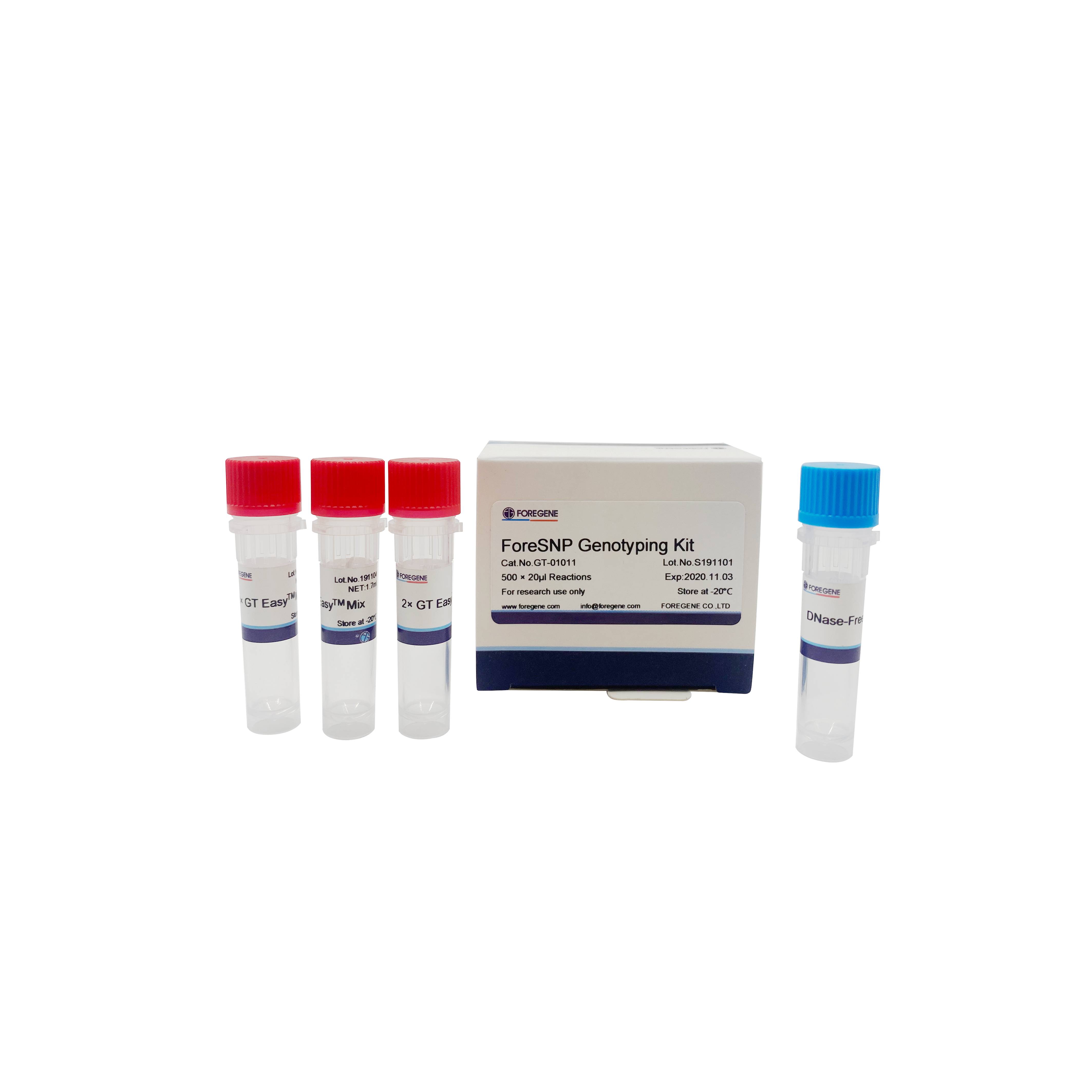
Kitaren osagaiak
| 2× GT ErrazaTMNahastu |
| DNasarik gabeko ddH2O |
| Argibideak |
Ezaugarriak eta abantailak
■Zehaztasun handia: kontrol positiboa idazten, zehaztasun-tasa% 98tik gorakoa da.
■ Kostu baxua: Ez da etiketa bikoitzeko zunda garesti ugari sintetizatu beharrik.
■ PCR sistema optimizatua: sistemaren egonkortasun ona eta anplifikazio espezifikotasun handia.
■ Kutsaduraren aurkako PCR sistema: PCR produktuek eragindako aerosol kutsadura modu eraginkorrean ezaba dezake, ingurumenaren kutsaduraren interferentziaz arduratu gabe kontrol negatiboaren seinale fluoreszentearen gainean, eta anplifikazioaren espezifikotasuna eta idazketaren zehaztasuna bermatu gabe.
Kit aplikazioa
Araztutako DNA laginak genotipatzeko probetan erabiltzeko pentsatua.
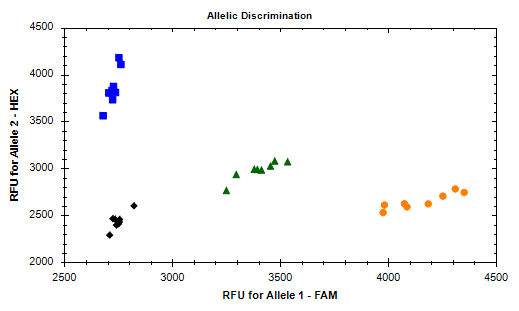
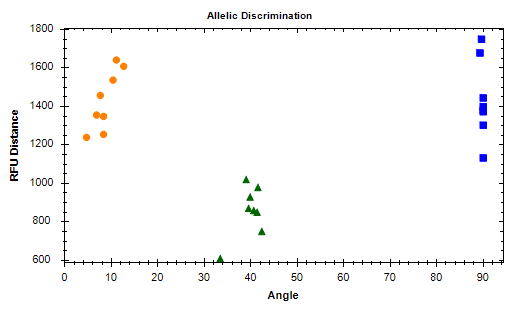
Adibidea
Esperimentu honetan, 200 ng-ko gariaren DNA genomikoa erabili zen txantiloi gisa, Foresnp Genotyping Kit-aren arabera gariaren alearen pisuarekin erlazionatutako TaGS-D1 genearen tipifikazioa detektatzeko.Instrumentuaren eredua BIO-RAD CFX connect da;lagin kopurua 21 da, NTC kopurua 8 eta kontrol positibo mota bakoitza 1 da.
ForeSNP Genotipatzeko Kita